Pour la première fois, Patrick Edery du Centre de recherche en neurosciences de Lyon (Inserm/CNRS/Université de Lyon 1), Anne-Louise Leutenegger de l’unité Inserm 946 « Variabilité génétique et maladies humaines » à Paris et leurs collaborateurs ont décrit un nouveau groupe de mutations génétiques grâce au séquençage du génome. Les chercheurs ont montré l’implication d’un petit ARN dans une maladie génétique chez l’Homme (syndrome de Taybi-Linder). Ce petit ARN, appelé ARNsn – pour Small Nuclear ARN – intervient lors d’une étape cruciale qui précède la synthèse des protéines. La découverte de mutations sur l’ARNsn permettrait à terme l’identification rapide de gènes impliqués dans le développement du cerveau, des os et d’autres tissus. Des perspectives thérapeutiques pourraient en découler. Ces résultats sont publiés dans la revue Science datée du 8 avril 2011.
Lors du développement embryonnaire, l’information génétique supportée par l’acide désoxyribonucléique (ADN), organisé en gènes, subit plusieurs opérations qui mènent à la synthèse des protéines qui constituent l’organisme.
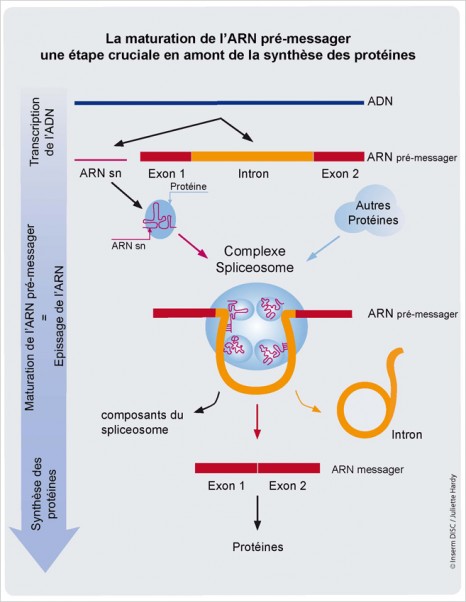
Cette information est d’abord transcrite en acide ribonucléique (ARN) messager puis traduite en protéines. Chez les eucaryotes, il existe une étape intermédiaire de maturation de l’ARN pré-messager. Ce processus, connu sous le nom d’ « épissage de l’ARN », est rendu possible par l’action du « spliceosome », un outil particulier constitué de petits ARNsn (1) et de protéines. Ce complexe permet d’enlever les parties non codantes de l’ARN pré-messager que l’on appelle « introns » et de souder celles qui sont codantes, appelées « exons », qui seront utilisées lors de la synthèse des protéines (Figure ci-contre).
La maturation de l’ARN pré-messager, une étape cruciale en amont de la synthèse des protéines © Inserm / J.Hardy
Les chercheurs révèlent ici une anomalie au sein du « spliceosome » qui est un acteur essentiel en amont de la synthèse des protéines, dès le développement embryonnaire et durant toute la vie pré- et postnatale.
Les scientifiques ont identifié une anomalie au niveau d’un des petits ARNsn du spliceosome chez des patients présentant un décès rapide post-natal et des malformations graves du cerveau, des os et d’autres tissus (nanisme microcéphalique primordial de type 1, MOPD1, ou syndrome de Taybi-Linder, TALS). « Dans un premier temps, l’utilisation d’une nouvelle méthode statistique (2) a permis de localiser le défaut génétique sur une petite région du chromosome 2. Ensuite, les dernières techniques de séquençage haut-débit ont rendu possible l’identification de 4 mutations liées à l’ARNsn dont le nom est U4atac », souligne Anne Louise Leutenegger. Selon les chercheurs, ces mutations sont responsables de la mort précoce quelques mois après la naissance et des malformations sévères du cerveau et des os, observées chez les patients atteints du syndrome de Taybi-Linder (3).
« Grâce à cette découverte, il est maintenant possible de proposer un diagnostic prénatal précoce de cette affection très grave, mais au-delà, l’identification des protéines perturbées par cette anomalie pourrait permettre d’envisager des stratégies thérapeutiques permettant d’éviter le décès », explique Patrick Edery.
Plus important encore, il s’agit de la première implication d’un petit ARNsn du complexe « spliceosome » dans une maladie génétique. Ce travail indique qu’un épissage efficace, c’est-à-dire la maturation de l’ARN pré-messager, est nécessaire pour un développement embryonnaire normal et pour la vie post-natale chez l’homme. En effet, une anomalie observée en amont de la synthèse des protéines a des répercutions importantes sur l’ensemble des étapes du développement embryonnaire et postnatal des individus.
« La découverte de ce nouveau mécanisme responsable d’anomalies du développement devrait permettre, grâce à la technique de séquençage du génome, d’identifier de nombreux gènes impliqués dans de graves malformations génétiques », conclut Patrick Edery.
Notes
(1) ARNsn : Small Nuclear Ribonucleic Acid / Petit Acide RiboNucléique contenu dans le noyau de la cellule
(2) Using genomic inbreeding coefficient estimates for homozygosity mapping of rare recessive traits: application to Taybi-Linder syndrome – Leutenegger AL, Labalme A, Genin E, Toutain A, Steichen E, Clerget-Darpoux F, Edery P. – Am J Hum Genet. 2006; 79(1):62-6
(3) MOPD1 ou syndrome de Taybi-Linder : une maladie génétique grave pouvant induire un décès juste après la naissance ou des malformations graves du cerveau, des os et d’autres tissus. A ce jour, la prévalence de la maladie est inconnue et environ 30 cas ont été décrits dans la littérature